 |
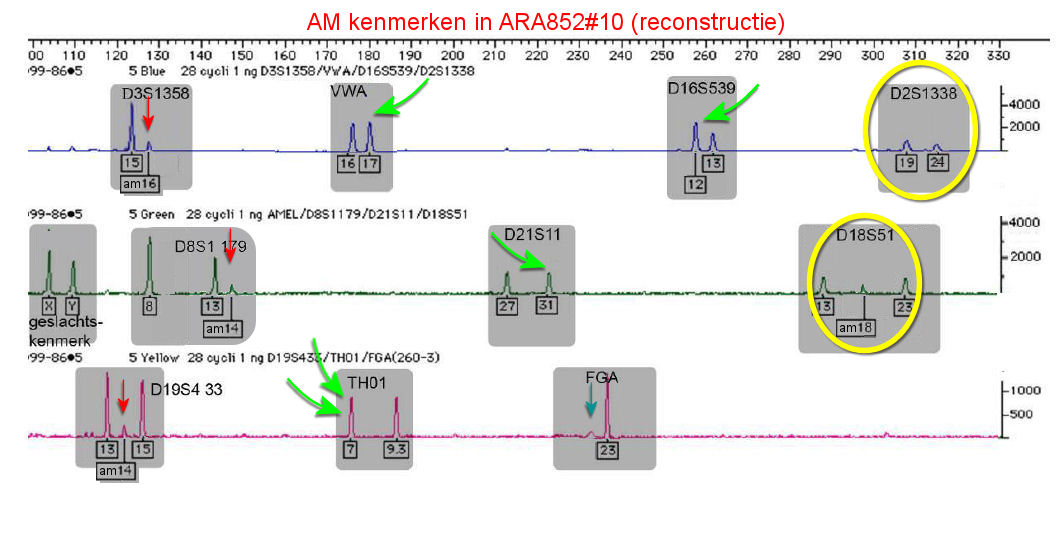
| Deze reconstructie van het
electroferogram van spoor #10 laat de ligging van de 11 loci
zien, die later door een computer werden teruggevonden. |
Spoor #10 in de computer |
Het NFI heeft van spoor #10 alleen gerapporteerd, dat spoor #10 overeenstemt met het profiel van Louwes. Verder niets. Pas tijdens de herzieningsaanvraag in 2006 kwam daar enige wijziging in. Uit de overlegde electroferogrammen werd het ten kantore van Prof. Mr. Knoops duidelijk, dat er op meerdere posities in het electroferogram extra piekjes zichtbaar waren, die uitgelegd konden worden als een minimaal spoor van DNA van het slachtoffer. Deze waren door de NFI-onderzoeker van het electroferogram speciaal gesignaleerd door middel van een zogenaamd am-label, dus added manually. In twee gevallen precies op posities, waar het slachtoffer in haar profiel dubbele pieken toonde: D3 en D8.
 |
| Deze reconstructie van het
electroferogram van spoor #10 laat de ligging van de 11 loci
zien, die later door een computer werden teruggevonden. |
Sindsdien is er heel wat veranderd in DNA-land. Waardoor de DNA-analyses veel trefzekerder zijn geworden. Er wordt tegenwoordig niet alleen gelet op de posities, die de pieken innemen, maar ook hoe hoog ze zijn. Paragraaf 6.3 en de onderliggende paragrafen geven daar al een idee van. Maar het kan nog beter met behulp van de computer. De computer kan allerlei complicaties, die ontstaan bij het maken van een profiel op waarde schatten (letterlijk) en verwerken in een totale uitkomst, zo in de trend van: hoe waarschijnlijk is dit profiel eigenlijk als we uitgaan van dit en dat? Dit en dat kunnen we zelf dan invullen.
En dat gaan we hier doen, want we hebben profiel #10 beschikbaar en kunnen vervolgens een dit en een dat definiëren:
Om het verhaal niet verder te compliceren richten we hier ons op twee
computerprogramma's, die in wezen hetzelfde verrichten. De ene komt van de
universiteit van Oslo en heet EuroForMix. De andere is geïntroduceerd door
het NFI en heet DNAstatistX. Afgezien van technische details (gebruikte
programmeertalen) doen ze precies hetzelfde. Omdat het NFI veel te maken
heeft met de voorliggende vragen, richten we ons hier vooral op
DNAstatistX, dat welwillend door het NFI ter beschikking werd gesteld.
Wie het naadje van de kous wil weten leest het hele verhaal hier:Uitgerekend spoor #10.
De bediening is erg eenvoudig. Twee
'kommagescheiden' tekstbestanden volstaan. Het ene geeft het profiel weer,
van alle piekjes die je kunt onderscheiden de hoogte en de plekken waar ze
staan. Het andere bestand bevat de referentieprofielen, die zijn nog
eenvoudiger, alleen de plaatsen waar de pieken staan zijn genoeg.
Daarnaast moet je nog opgeven welke DNA kit werd gebruikt en welke
drempelwaarden worden aangehouden - die mag je kiezen, waardoor je
meerdere mogelijkheden kunt laten onderzoeken. Het belang van dergelijke
waarden werd in de beeldbank uitgelegd. Voorts moet nog een bestand met
frequenties van markers worden aangegeven (wellicht in het onderhavige
geval overbodig).
Vervolgens kies je de Hp en de Hd, ofwel, welke referentieprofielen in
aanmerking komen als 'bouwstenen' voor het voorliggende profiel. Daarna
kun je de twee mogelijkheden laten aftasten.
De computer gaat piek voor piek na, welke
(on-)waarschijnlijkheden moeten worden ingecalculeerd om de gevonden
hoogte te rechtvaardigen. We zagen hierboven al, dat er een paar pieken
zijn, die niet uit het profiel van Louwes stammen, dus de Hp staat al bij
voorbaat op losse schroeven. Maar er is meer, in de paragraaf spoor #10 onder loep is dat voor vele pieken al
gedemonstreerd. Nu de computer nog.
Na de aangevraagde berekening komt de computer met twee
waarschijnlijkheden: Hp laat zien, hoe veel toeval nodig is om precies dat
profiel als we hierboven zien tevoorschijn te toveren. En dat is veel
toeval, zo ongeveer 1 op een getal met ruim 90 nullen. Ook de Hd geeft een
heel kleine waarde, maar tco wel wat groter dan de Hp. De verhouding
schommelt - afhankelijk van de gekozen drempelwaarden - zo tussen de 1 op
3 en 1 op 400. Maar altijd ten gunste van Hd. Wat hier logisch wordt
gevonden, spoor #10 is een mengprofiel, vindt de computer(software) ook
logisch. En zou het NFI ook logisch moeten vinden, want het is hun
software.
 |
 |
 |
|
| Links het
electroferogram van de computer. Met de muis kan men in het
gebruikte programma EuroForMix de pieken selecteren en
uitvergroten en op die manier de bijdragen aan het profiel van
de twee donoren zichtbaar maken. Rechts een afbeelding uit DNAStatistX, die de totale bijdragen van de twee donoren laat zien. Zoals al gesteld, kan het bloedvlekje van mevrouw Wittenberg prima worden vereenzelvigd met de hoeveelheid DNA van haar in het mengsel. |
|||
 |
 |
|
| Links het
electroferogram afgeleid uit EuroForMix. Rechts het profiel uit
spoor #6 dat zonder aarzeling aan het slachtoffer werd
toegeschreven. In beide profielen van (even-)lage RFU-waarden
ontbreken pieken (dropouts) maar zijn er ook genoeg over. In het
linker diagram staat geen Xamel, maar dat is een
(computer-)technische kwestie. |
||